(Viene de la segunda parte)
Influenza virus
Antes de la COVID-19, el virus de la gripe (Orthomyxoviridae o influenza virus, descubierto en 1931 por Richard Shope) era el candidato numero uno a desencadenar la siguiente pandemia. Y posiblemente lo sigue siendo, aunque ahora, con las cercanas epidemias de SARS y MERS y la actual pandemia de COVID, se podría discutir si los coronavirus disputan a influenza el titulo de clase de virus más peligroso. Al igual que el SARS-CoV-2, el material genético de influenza virus es RNA, ambos se transmiten eficazmente por la vía respiratoria mediante aerosoles y ambos pueden contagiarse de persona a persona justo antes de que se presenten síntomas (aunque en el caso del SARS-CoV-2 el periodo de tiempo contagioso antes de presentar síntomas es más largo que el de influenza).
Todas estas características hacen que ciertas clases de coronavirus e influenza virus sean particularmente peligrosos. Influenza virus tiene una importante propiedad adicional: su genoma de RNA esta dividido en segmentos que pueden barajarse (reagruparse, en terminología técnica) de manera que si dos virus distintos infectan la misma célula se pueden generar nuevas partículas de virus con segmentos intercambiados, lo que incrementa la capacidad de variación y por tanto el potencial de generar nuevos virus peligrosos. La extraordinaria capacidad de variación de influenza virus por reagrupamiento de los segmentos de su genoma, además de mutación de los mismos, es la razón por la que las vacunas contra la gripe tienen que renovarse cada año.
Orthomyxoviridae incluye cuatro géneros de virus principales que infectan toda clase de animales terrestres y acuáticos. Dos de ellos, influenza virus A y B, son responsables de las epidemias estacionales en humanos, pero es influenza virus A la que causa pandemias globales, puesto que tiene superior capacidad de variación e infecta también otras especies. Patos, gansos, ocas y otras aves acuáticas son reservorios naturales de la mayoría de influenza virus A, pero también infectan aves de corral y muchos otros animales como cerdos, perros, caballos, focas, ballenas etc.
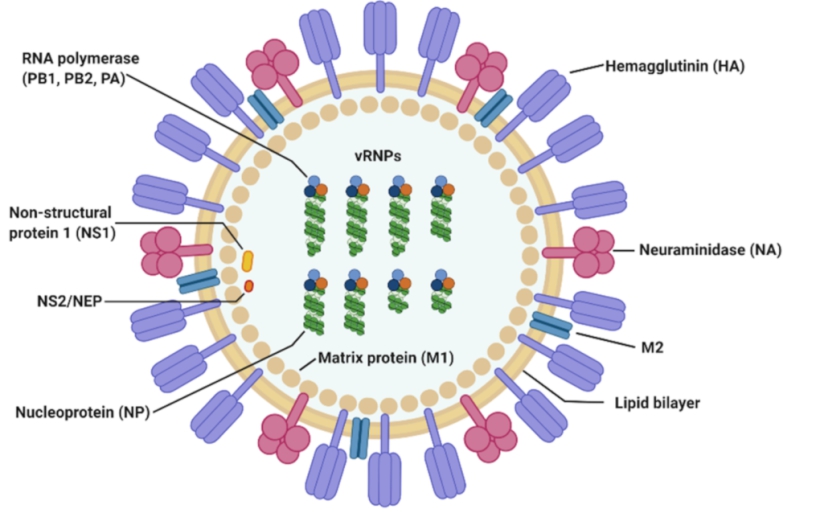
Influenza virus A se clasifica en distintos subtipos dependiendo de dos glicoproteínas de la superficie vírica: hemaglutinina (H), utilizada por el virus para unirse al receptor y penetrar la célula, y neuraminidase utilizada por el virus para salir de la célula infectada después de replicarse. Hay 18 subtipos de hemaglutinina (H1-H18) y 11 subtipos de neuraminidase (N1-N11), pudiendo dar lugar a un total de 198 combinaciones posibles, de las cuales se han detectado 131 en la naturaleza. Aunque tres combinaciones han causado pandemias recientes (ver tabla), solo dos de ellas H1N1 y H3N2, circulan actualmente de manera amplia en humanos. Variaciones en estas dos ultimas son responsables de las gripes estacionales que causan entre 290 000 y 650 000 muertes por año (dato de la Organización Mundial de la Salud), a pesar de cierto grado de inmunidad proporcionado por anteriores gripes. Las vacunas anuales están diseñadas contra epítopos en glicoproteínas de H1N1 H3N2 en influenza A, así como epítopos de influenza virus B, y su administración es esencial para prevenir muchísimas muertes y hospitalizaciones.
A diferencia de las típicas gripes estacionales, causadas por variaciones (mutaciones) relativamente limitadas en influenza A virus que circulaban ya entre la población, las pandemias están causadas por influenza virus A diferentes a los que circulan contemporáneamente en la población, por lo que hay pocas defensas contra ellos. Estos nuevos virus se pueden generar por procesos de intercambio de segmento (reagrupamiento) entre virus de animales (aves, cerdos) y virus que ya circulaban en poblaciones humanas. Para desencadenar una pandemia, estos nuevos virus deben de poder infectar a humanos y transmitirse entre ellos, lo que implica adaptarse a los receptores humanos de hemaglutinina; afortunadamente esto no ocurre de manera frecuente
Las pandemias de gripe seguramente han azotado a la humanidad de manera cíclica desde tiempo inmemorial, aunque antes del siglo XX no teníamos los conocimientos científicos ni la tecnología para distinguir influenza de otros virus que actuasen por vía respiratoria y causaran sintomatología parecida como vimos que pudiera haber sido el caso de la gripe rusa de 1889.
| Nombre de la pandemia | Fecha | Muertes | Case Fatality Ratio | Subtipo virus |
| Gripe rusa | 1989-90 | 1 millón | 0.1% | ? |
| Gripe española | 1918-20 | 40-100 millones | 2-3% | H1N1 |
| Gripe asiática | 1957-58 | 1-1.5 millones | 0.13% | H2N2 |
| Gripe de Hong Kong | 1968-69 | 1 millón | <0.1% | H3N2 |
| Gripe porcina | 2009-10 | 0.3 millón | 0.03% | H1N1 |
Tabla 1. Epidemias contemporáneas causadas por Influenza virus
La historia y periodicidad de las pandemias de gripe nos indican que, con seguridad, vendrán mas en un futuro mas o menos próximo. Afortunadamente, estamos mejor preparados para ella que en cualquier tiempo pasado porque la Organización Mundial de la Salud (WHO, Global Influenza Surveillance and Response System) y otras organizaciones constantemente vigilan y estudian los influenza virus A que circulan entre las aves y otros animales. Estirpes de influenza detectadas en aves en los últimos treinta años incluyen H7N7, H7N9, H9N2 y H10N3, pero los casos de humanos infectados con estas estirpes son de momento relativamente raros y producidos por repetido contacto con las aves y no por transmisión de humano a humano.
Las estirpes H2N2 causantes de la gripe asiática de los años 50 han desaparecido de la circulación, por lo que la inmensa mayoría de la población no tiene inmunidad contra esta estirpe. Esto la hace peligrosa, puesto que H2N2 perdura en aves salvajes y de corral y sabemos que tiene potencial pandémico como ya demostró en el pasado. El peligro mas cercano proviene de las variantes mas prevalentes que ahora circulan globalmente entre las aves acuáticas, variantes del tipo H5Ny (H5N1, H5N2, H5N6 H5N8). En varias ocasiones han saltado a aves de corral entre las que causa estragos con mortalidades cercanas al 100 %.
A causa de la alta prevalencia en aves, ha habido numerosos casos de H5Ny en humanos, causando muertes entre personas en contacto directo y continuo con las aves (WHO, Global Influenza Surveillance and Response System), pero afortunadamente parece que la transmisión entre humanos de esta variante es de momento extraordinariamente rara o inexistente. El gran peligro es que H5Ny se reagrupase con virus humanos en un animal y adquiriese la capacidad de infectar y transmitirse eficazmente en humanos. Con esto en mente, Estados Unidos y otros gobiernos han producido y almacenado vacunas en previsión de una futura pandemia H5Ny… aunque el virus que haga el salto pudiera escaparse por mutación a las vacunas almacenadas.
La nueva tecnología de vacunas de RNA mejorará notablemente nuestra capacidad de defendernos contra las gripes, ya sean estacionales anuales o pandémicas. Un problema actual es que para producir a gran escala las vacunas convencionales se requieren al menos seis meses desde que los centros de vigilancia de la gripe distribuidos por todo el mundo, incluidos los de la Organización Mundial de la Salud (WHO), identifican nuevos virus de la gripe hasta que se produce una vacuna especifica contra esos virus (normalmente se generan vacunas contra los cuatro virus predominantes).
Esto se debe a que la mayoría de las vacunas se producen inyectando los virus en huevos de gallina que funcionan como incubadores. Los virus son entonces inactivados y el antígeno purificado. Aunque algo mas rápida, la tecnología de incubar los virus en células en cultivo es también lenta. Este tiempo a veces disminuye la efectividad de la vacuna, pues la estirpe predominante del virus ha cambiado. Las vacunas de mRNA son mucho mas rápidas de producir, y por tanto la capacidad de respuesta y la probabilidad de la vacuna de ser efectiva contra el nuevo virus será mayor que con las vacunas fabricadas por los métodos convencionales.
¿Es posible desarrollar una vacuna universal contra la gripe? Las actuales vacunas contra las gripes estacionales están dirigidas contra epítopos de alta inmunogenicidad que desafortunadamente resultan ser muy variables, por lo que las vacunas necesitan constante renovación. Los epítopos poco variables conocidos resultan ser de baja inmunogenicidad y por tanto no son ideales para el desarrollo de vacunas, puesto que requerirían constante reinmunización.
Una potencial vacuna universal debería estar dirigida contra un epítopo de alta inmunogenicidad y baja variabilidad. ¿Pero existen? Un argumento en favor de la hipótesis de que existen es la observación de que hay relativamente poca variación genética de influenza virus que circulan entre las poblaciones si consideramos todas las posibilidades teóricas de variación. Esta paradoja se puede explicar con la hipótesis anterior, puesto que la mayoría de nuevos virus no podría expandirse en las poblaciones animales y humanas debido a respuestas inmunes contra epítopos de limitada variabilidad. Un estudio reciente en grupos de niños demostró que tenían inmunidad natural contra estirpes de influenza virus del pasado a los que nunca estuvieron expuestos y que esta inmunidad se basaba en un epítopo conservado de H1 (PMID: 30242149). Si estos estudios se confirman, demostrarían la existencia de epítopos de alta inmunogenicidad y baja variabilidad y abrirían la puerta para vacunas universales contra muchos tipos de influenza virus.
Otros virus amenazantes con potencial pandémico
Cuando pensamos en virus peligrosos, ébola y virus de Marburg nos vienen a la cabeza por las terroríficas consecuencias que conllevan sus infecciones, entre ellas fiebres hemorrágicas y mortalidades altísimas. Menos conocidos en Occidente, pero también letales, son Nipah y Hendra. Todos ellos tienen en común un origen zoonótico (sus huéspedes naturales son animales y en algún momento saltaron a humanos en estrecho contacto con la especie huésped), como lo tuvieron en su momento el virus del sarampión y mas recientemente el del sida.
En 1994, una misteriosa enfermedad respiratoria y neurológica causó estragos entre caballos y acabó también con la vida del veterinario que los atendía en Hendra, un suburbio de Brisbane en Australia. Media docena de personas más fallecieron después, todos ellos cuidadores de los caballos. El origen de la enfermedad resultó ser un virus transmitido por zorros voladores (murciélagos frugívoros del genero Pteropus) que frecuentaban higueras bajo las que pastaban los caballos. Poco después, en 1999, se identificó un virus relacionado con el de Hendra (de la familia de Paramyoxivirus) que causó estragos en millones de cerdos en Malasia, llegando a contagiar a granjeros que los cuidaban, pero sin que hubiese transmisión de persona a persona.
Sin embargo, este nuevo virus, llamado Nipah, resultó ser el mismo responsable de brotes infecciosos anuales en Bangladesh y la India. Estos brotes afectaban a personas que habían bebido savia de palmera o comido fruta contaminada con fluidos corporales (orina, saliva, sangre) de los zorros voladores e incluso a personas que habían trepado a los arboles donde se refugiaban los murciélagos. A diferencia del virus de Hendra, hay abundante evidencia de la transmisión de persona a persona en el caso de Nipah; en un caso reciente y bien documentado un brote infeccioso en Kerala (India) en mayo-junio de 2018, llevó a la hospitalización de un paciente que contagió a familiares y a otros pacientes del hospital con el resultado de que fallecieron 21 de 23 personas afectadas (PMID: 30364984).
Afortunadamente, Nipah, Ebola, Margburg y otros virus peligrosos como el sida solo se transmiten mediante contacto con fluidos corporales, lo que limita enormemente su potencial epidémico. El contagio de persona a persona observado en múltiples casos de Nipah es sin embargo preocupante, porque que en algunos casos pudieran deberse a microgotas respiratorias producidas por infectados en contacto estrecho y continuado con familiares o en ambulatorios. Recordemos que los virus del sarampión y de las paperas, como Nipah también de la familia Paramyoxivirus, evolucionaron para transmitirse entre humanos con altísimas tasas de contagio. Son estos virus que se trasmiten eficazmente a través del aire en aerosoles (como por ejemplo influenza, coronavirus o el virus del sarampión), los de mayor potencial pandémico.
Los virus transmitidos por vectores, por ejemplo, mosquitos, también tienen considerable potencial pandémico. Entre ellos están el virus del Nilo occidental, zika, dengue, fiebre amarilla y chikingunya, todos los cuales pueden causar un rango de patologías que van desde las leves o asintomáticas a las muy graves como microcefalia (zika), encefalitis (virus del Nilo), fiebres hemorrágicas (dengue), o artritis crónica (chikingunya) y en conjunto causan muchas decenas de miles de muertes anuales en zonas tropicales. Los países ricos del hemisferio norte han estado históricamente mas o menos a salvo, pero con el calentamiento global especies de mosquitos que solo habitaban zonas tropicales o subtropicales están alcanzando nuestras latitudes, como hemos visto recientemente con el mosquito del Nilo en Andalucía.
Virus X desconocido
Aunque sea complicado y lleno de múltiples obstáculos, podemos prepararnos para futuras pandemias de virus conocidos como influenza, coronavirus o virus transmitidos por mosquitos y otros vectores. En el caso de influenza, como escribimos más arriba, hay un sistema en marcha de vigilancia para supervisar su presencia en sus reservorios animales (Global Influenza Surveillance and Response System). Una posible opción para detectar nuevas pandemias de otros virus conocidos sería aprovechar muestras sobrantes de sangre recogidas por motivos rutinarios en ambulatorios y hospitales de todo el mundo para investigar la posible presencia de anticuerpos contra estos virus. De esta manera se podría medir la prevalencia de infecciones en distintos lugares del globo y detectar brotes infecciosos antes del estallido pandémico.
Esto solo es posible con los virus conocidos, puesto que sabemos reconocer los anticuerpos con los que nuestro sistema inmunitario se defiende de ellos. Pero ¿y si la próxima pandemia no proviene de un coronavirus, influenza u otro virus conocido sino de uno del que no sabemos nada? ¿Cómo defendernos contra un virus con potencial pandémico que desconocemos? En este caso no podemos detectar anticuerpos contra ellos, pero afortunadamente disponemos de tecnología genética para hacerlo.
La metagenomica es el estudio de una colección de material genético (genomas) proveniente de una comunidad mezclada de organismos. Gracias a las nuevas y ultrarrápidas técnicas de secuenciación del DNA y a sofisticadas herramientas bioinformáticas, podemos recoger muestras de cualquier medio ambiente, incluido tejidos o fluidos humanos, y secuenciar su contenido en DNA para después recomponerlo y clasificarlo como perteneciente a distintas formas de vida conocidas o desconocidas. Este tipo de tecnología fue de hecho la que permitió secuenciar el genoma del SARS-CoV-2 a partir de muestras del tracto respiratorio en pacientes con neumonía en Wuhan, China (PMID: 31978945).









Interesantísimo artículo (colección de artículos).
Si nos decantásemos por leer este tipo de informaciones (y no las bazofias sensacionalistas que abundan en los medios generalistas) el comportamiento y opinión de la población sin duda mejoraría.
Enhorabuena y gracias al autor, Juan Botas, por el esfuerzo didáctico, y a JotDown por la publicación.
Saludos.
Enhorabuena por el artículo, de una calidad en sus explicaciones de altísimo nivel, así como sus links a los papers científicos que lo avalan. Da gusto leer este tipo de informaciones en un medio generalista.